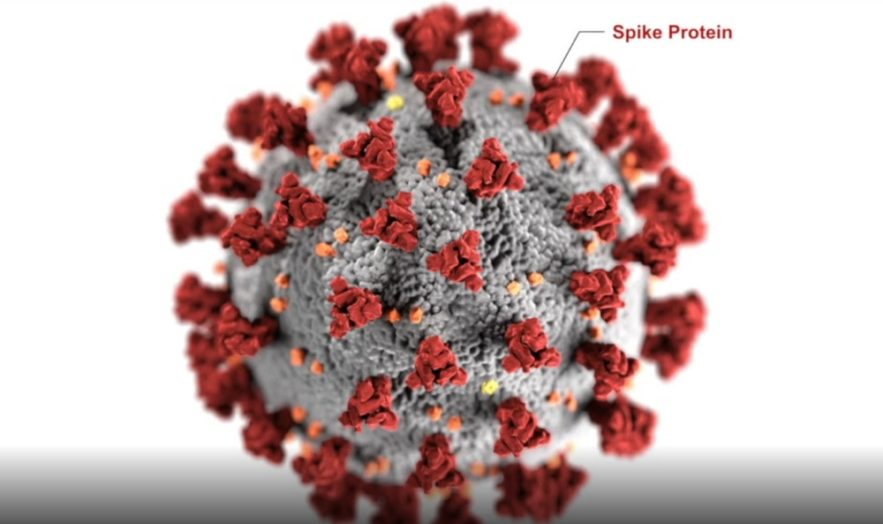
La protéine de pointe du SARS-CoV-2 permet au nouveau coronavirus de pénétrer dans les cellules humaines. Elle est donc au cœur des recherches dans le monde entier. Une équipe internationale de chercheurs propose aujourd’hui le tout premier modèle open source complet de cette protéine, ce qui permettra à toute la communauté scientifique d’effectuer diverses simulations dans le cadre de leurs recherches autour du COVID-19.
La protéine de pointe (ou protéine S) permet l’entrée virale dans les cellules hôtes lorsque son domaine de liaison au récepteur interagit avec l’enzyme de conversion de l’angiotensine humaine 2 (ACE2). En raison de son rôle majeur dans l’infection, la protéine S est l’une des cibles principales pour le développement de vaccins et de médicaments antiviraux.
Une protéine complexe, complètement modélisée
Une vidéo de démonstration explique aux spécialistes concernés comment construire un modèle de protéine de pointe pleinement glycosylée – autrement dit, liée à différents glucides – sur une membrane virale :
Ce programme de construction est en accès libre et peut être téléchargé sur le site du projet CHARMM-GUI. Les auteurs du projet se proposent même de créer d’autres systèmes à la demande, selon les besoins.
Développé par Wonpil Im, professeur au département de bio-ingénierie de l’Université de Lehigh, CHARMM-GUI est un programme qui simule les systèmes biomoléculaires complexes simplement, précisément et rapidement. Im le décrit comme un « microscope informatique », qui permet aux scientifiques de comprendre les interactions au niveau moléculaire, qui ne peuvent être observées autrement.
Les modèles développés par Im et ses collaborateurs – le Dr Chaok Seok de l’Université nationale de Séoul et le Dr Tristan Croll de l’Université de Cambridge – sont les premiers modèles de protéines de pointe (ou « protéines S ») du SARS-CoV-2 entièrement glycosylées, mis à disposition de tous les scientifiques. C’est le fruit d’un travail fastidieux consistant à construire des modèles de haute qualité à partir des parties connues de la structure obtenue par cryomicroscopie électronique (cryo-EM).
En effet, la structure de la protéine S a auparavant été déterminée par cryo-EM, avec le domaine de liaison au récepteur orienté vers le haut et aussi vers le bas, mais ces modèles présentaient plusieurs lacunes. Ainsi, Im et ses collègues ont modélisé les résidus d’acides aminés manquants, puis d’autres éléments manquants tels que les glycanes (glucides) potentiellement liés à la protéine S. À noter que ces glycanes nuisent à la fonction des anticorps, qui peinent à reconnaître l’intrus… C’est la raison pour laquelle le développement d’un vaccin est particulièrement complexe dans ce cas. De tels modèles faciliteront donc les recherches en la matière.
Les chercheurs proposent également un système de membrane virale d’une protéine S, qui sera particulièrement utile à leurs pairs dans le cadre de simulations de la dynamique moléculaire.
Une « science ouverte » pour faire avancer la recherche
La structure complète de la protéine S comprend un peptide de fusion (FP), des répétitions d’heptade 1 et 2 (HR1 et HR2), un domaine transmembranaire (TM) et cytoplasmique (CP). Au total, Im et ses collaborateurs mettent à disposition 8 modèles de protéines S complètes et entièrement glycosylées. Ils proposent également un modèle de la pointe uniquement.
Les modèles sont proposés au format PDB – Protein Data Bank, un format décrivant les structures moléculaires 3D – qu’il est possible de modifier et de manipuler selon ses besoins. C’est le principe même de l’édition open source : le code source est rendu public afin que chacun puisse y accéder et le modifier comme bon lui semble.
L’initiative de Im et son équipe fait écho aux recommandations de l’UNESCO, qui appelait, fin mars, à un meilleur partage des connaissances scientifiques, notamment autour du SARS-CoV-2 et du COVID-19. Lors d’une réunion (à distance) regroupant pas moins de 122 pays, l’organisation a notamment soulevé la question de la « science ouverte » (ou open science). « La pandémie de COVID-19 nous fait prendre conscience de l’importance de la science à la fois en matière de recherche et de coopération internationale. Cette crise nous montre aussi l’urgence d’un meilleur partage des connaissances à travers la science ouverte. Il est temps de nous engager tous ensemble », déclarait Audrey Azoulay, Directrice générale de l’UNESCO.
Sur le même sujet : Coronavirus : Un modèle 3D précis de SARS-CoV-2 dévoilé
Le Docteur Soumya Swaminathan, scientifique en chef à l’Organisation mondiale de la Santé, a ajouté que la collaboration était essentielle pour la connaissance et le partage de données, ainsi que pour faire progresser la recherche sur le COVID-19. « Nous vaincrons la COVID-19 par la diffusion des connaissances en toute transparence », pouvait-on lire dans un communiqué du bureau européen de l’OMS fin avril. L’appel a été visiblement entendu puisqu’en quelques semaines, plus d’un millier d’articles de recherche scientifique ont été publiés en accès libre.