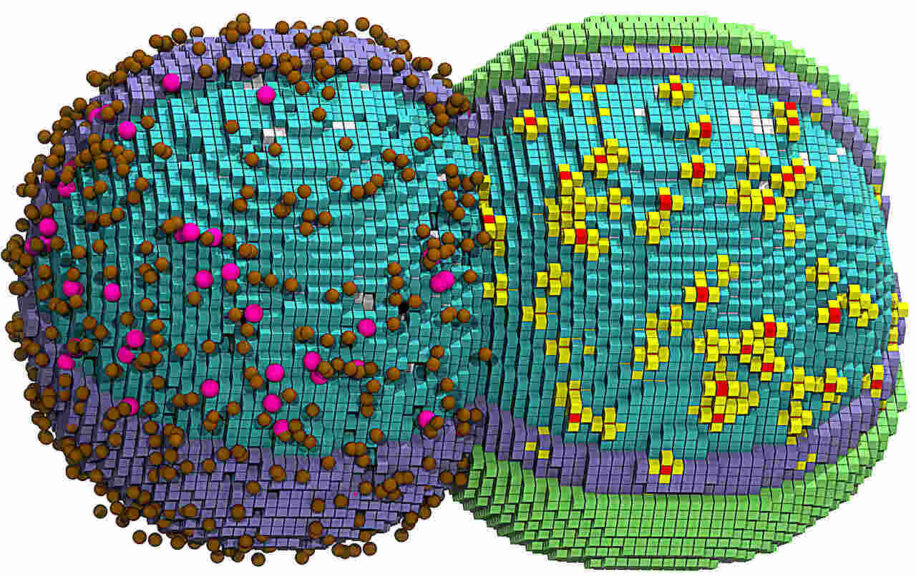
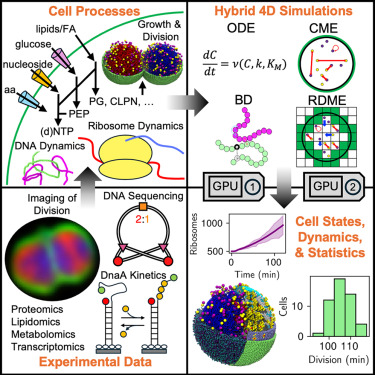
Des chercheurs ont simulé en 4D (dans le temps et dans l’espace) une cellule vivante à l’échelle nanométrique et reconstitué le comportement de chaque molécule qui la compose tout au long de son cycle de vie. La simulation a nécessité d’importantes ressources informatiques, la reproduction du processus de réplication de l’ADN nécessitant à lui seul une unité de traitement graphique (GPU) spécifique. L’équipe a pu simuler un cycle cellulaire complet de 105 minutes en six jours de calcul.
La connaissance de l’ensemble des caractéristiques d’une cellule est essentielle à la compréhension des mécanismes complexes régissant son cycle de vie. Ces caractéristiques englobent les processus physiques et chimiques qui se synchronisent pour induire les différents changements d’état de la cellule et activer ses différentes fonctions.
Cependant, déterminer simultanément la composition moléculaire et l’architecture d’une cellule entière est actuellement impossible en une seule expérience. D’importantes avancées ont été réalisées à cet effet en matière de modélisation informatique en utilisant de vastes ensembles de données biologiques issus de nombreuses expériences.
Les avancées en matière d’IA ont également permis de constituer des instantanés d’états cellulaires distincts. Mais les instantanés générés à l’aide de ces méthodes résultent principalement de prédictions et ne permettent donc pas nécessairement de renseigner sur les processus biologiques précis se produisant au sein d’une cellule.
Bien que complexes et fastidieuses, les modélisations basées sur des données expérimentales saisissent mieux l’ensemble des fonctions et des réactions cellulaires. Une équipe co-dirigée par l’Université de l’Illinois à Urbana-Champaign est parvenue à simuler l’intégralité du cycle de vie d’une bactérie minimale, une cellule viable avec le moins de gènes possible.
« Il s’agit d’un modèle cinétique tridimensionnel et entièrement dynamique d’une cellule minimale vivante qui imite ce qui se passe dans la cellule réelle », explique dans un communiqué Zan Luthey-Schulten, professeur de chimie à l’Université de l’Illinois à Urbana-Champaign et coauteur de l’étude publiée récemment dans la revue Cell.
« Une entreprise d’une telle envergure n’a été possible que grâce aux efforts conjugués d’une multitude de collaborateurs de l’Université de l’Illinois et de la Harvard Medical School, où nous avons systématiquement modélisé le métabolisme essentiel et d’autres réseaux subcellulaires à travers une série de publications débutant en 2018 », ajoute-t-il.
Une simulation d’une complexité informatique extrême
L’équipe de Luthey-Schulten a simulé le cycle de vie de la cellule en utilisant une plateforme de calcul avancée, de vastes jeux de données expérimentales et diverses techniques expérimentales et informatiques. Afin de reproduire avec précision la chronologie des événements cellulaires, l’équipe a pris en compte chaque gène, protéine, molécule d’ARN et réaction chimique se produisant au sein de la cellule. Le modèle devait par exemple reproduire fidèlement les processus permettant à la cellule de doubler de volume avant la division cellulaire.
La cellule minimale utilisée est une bactérie appelée « Syn3A » et dont le génome a été modifié de façon à contenir moins de 500 gènes, tous situés sur une unique molécule d’ADN circulaire. Les gènes ont été réduits au minimum afin d’assurer uniquement les fonctions essentielles telles que la réplication de l’ADN, la croissance et la division cellulaire, ainsi que l’exécution de la plupart des autres fonctions vitales.
Syn3A est dépourvue de noyau, comme toutes les bactéries, et chaque molécule qui la compose est soit un composant de sa membrane externe, soit transportée à l’intérieur de la cellule depuis l’extérieur, soit assemblée dans le cytoplasme. Cependant, la densité de molécules composant la cellule est si élevée que les chercheurs ont été contraints de rendre certains composants invisibles pour pouvoir créer des images animées et en haute résolution des différents processus.
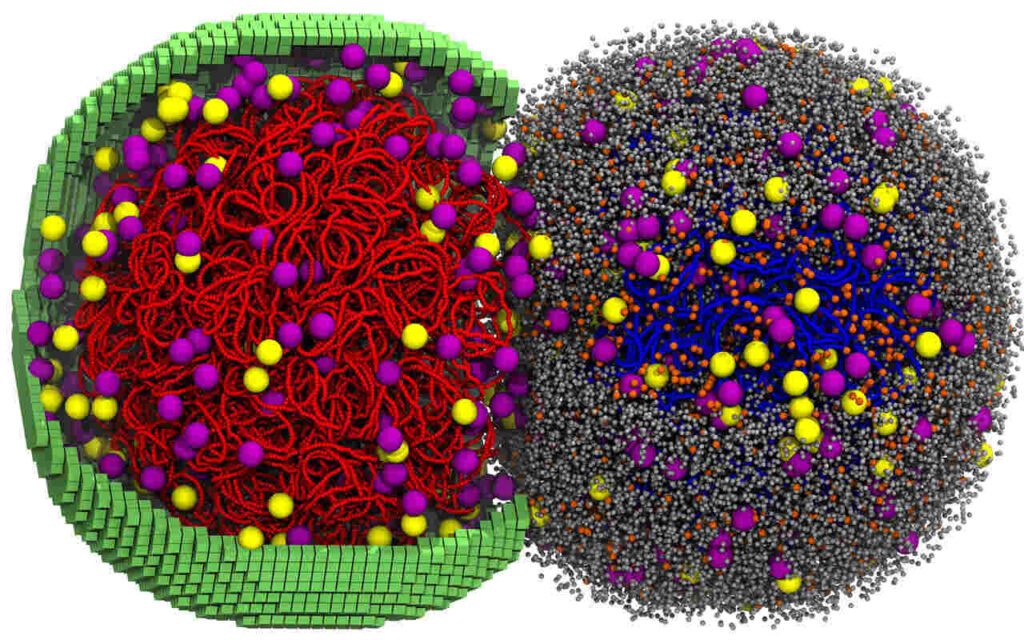
Les chercheurs ont par exemple pu observer comment le chromosome de Syn3A se déplace à travers l’intérieur complexe de la cellule en rendant invisibles toutes les protéines cellulaires. La simulation des mouvements et des événements cellulaires se produisant simultanément dans différentes parties de la cellule est en effet particulièrement complexe.
« Il est difficile de surestimer la complexité de la simulation de mouvements, et le faire en 3D pour une cellule entière a été… une véritable réussite », explique l’auteur principal de l’étude, Zane Thornburg, chercheur postdoctoral à l’Institut Beckman pour les sciences et technologies avancées et au Centre de cancérologie de l’Illinois. « L’un des derniers grands défis qu’Andrew [Andrew Maytin, étudiant diplômé du laboratoire de Luthey-Schulten] et moi avons dû relever a été de comprendre comment la membrane et l’ADN interagissent lorsqu’ils sont tous deux en mouvement. »


Des processus nécessitant plus de puissance de calcul que d’autres
D’autre part, certains processus nécessitaient plus de puissance de calcul que d’autres. Par exemple, la réplication des chromosomes ralentissait considérablement la simulation, doublant presque le temps nécessaire pour simuler l’intégralité du cycle cellulaire. Afin de pouvoir modéliser efficacement le processus de réplication de l’ADN, les chercheurs lui ont donc consacré un GPU spécifique, tandis qu’un autre GPU traitait tous les autres processus cellulaires. La stratégie a permis à l’équipe de simuler le cycle cellulaire complet de 105 minutes en six jours de calcul.
À noter toutefois que le cycle cellulaire simulé présente encore des limites dans la mesure où il ne s’agissait pas d’une simulation atome par atome, mais plutôt d’une moyenne de la dynamique des molécules individuelles. Néanmoins, il a permis de mettre en lumière de manière précise le déroulement des différents processus cellulaires.
Dans les simulations répétées impliquant des cellules individuelles avec des conditions initiales légèrement différentes, le cycle cellulaire simulé s’est déroulé, en moyenne, à deux minutes près du cycle cellulaire réel, a indiqué Thornburg.
« La capacité à saisir avec précision les conditions en constante évolution au sein d’une cellule vivante ouvre une nouvelle perspective sur les fondements des systèmes vivants », conclut Luthey-Schulten.
Vidéo de présentation de l’étude :